- 结果文件
- 使用指南
- 版本记录
- 联系客服
CHERRY可以基于多模态图 (multimodal graph)预测新发现病毒的宿主分类群(门到种)。病毒宿主预测是一种通过生物信息学方法来预测病毒可能感染的宿主物种。它的功能是根据病毒基因组的序列信息,分析宿主物种的基因组数据库,并通过比对和模式识别等算法来确定病毒可能感染的宿主。
示例文件:
待注释contig文件,后缀名为*.fasta、*.fa、*.fas、*.fna、*.fnn等,提交文件后设置长度截止阈值,要求>=3000bp,如:3000

小工具结果:
cherry_prediction.tsv :候选病毒序列宿主预测结果
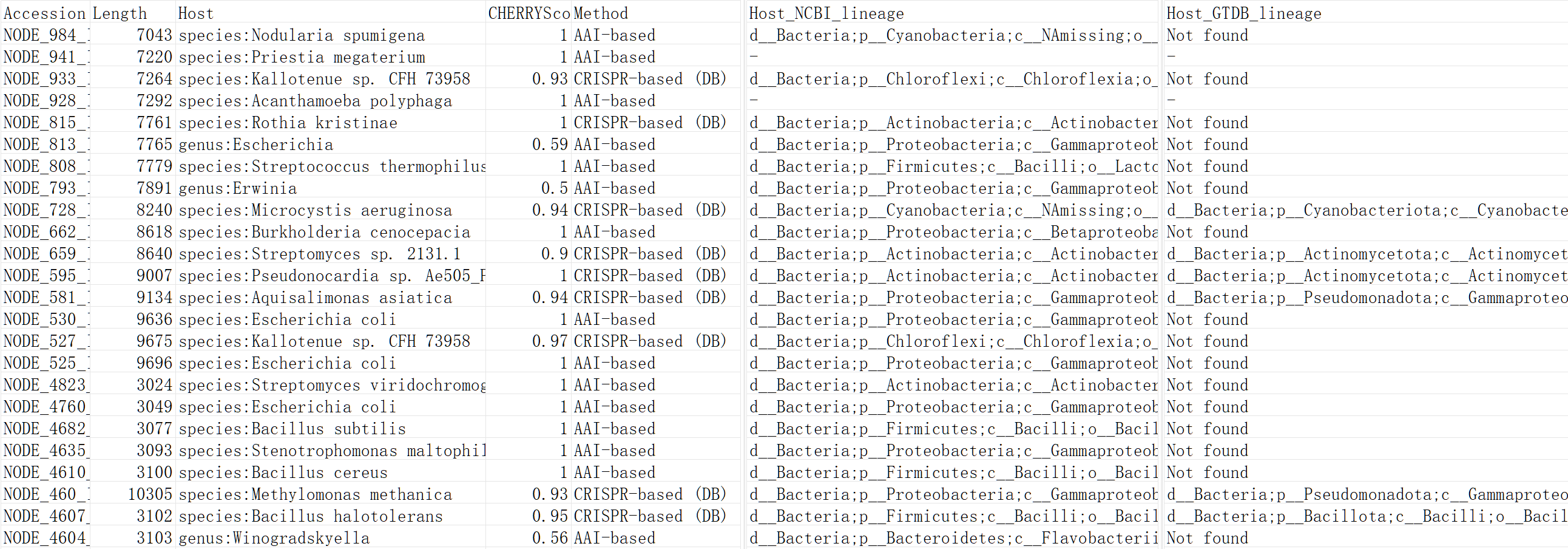
Accession:序列标识符;Length:序列长度(bp);Host:CHERRY预测该病毒最可能感染的宿主物种,-表示该序列未预测到宿主(可能是非病毒序列或模型无法识别);CHERRYScore:模型预测结果的置信度分数,范围通常为0-1,-表示无预测结果;Method:预测方法【① CRISPR-based(DB): CRISPRs alignment results from database;② AAI-based: predicting host based on virus-similarity】;Host_NCBI_lineage:预测宿主在NCBI数据库中的完整分类学信息;Host_GTDB_lineage:预测宿主在GTDB数据库中的完整分类学信息(Not found表示该物种在GTDB数据库中未找到对应记录)。
当前版本为1.0版本,上架时间为:2025-07-06